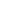Abb. 1
Unbalancierte Translokation zwischen den Chromosomen 4 und 12
a GTG-Bänderung: zusätzliche G‑dunkle Bande im distalen p‑Arm des derivativen Chromosoms 12 (Pfeil)
b Whole chromosome paint 4: Markierung des distalen p‑Arms des derivativen Chromosoms 12
c Array-CGH: partielle Monosomie 12p13.32-pter (SurePrint G3 ISCA CGH+SNP 180k Array der Firma Agilent, durchschnittlicher Abstand der Oligonukleotid-Array-Marker: 4,3 kb in Regionen besonderer klinischer Relevanz laut ISCA-Konsortium, 30,5 kb im restlichen euchromatischen Genom. Durchschnittliche technische Auflösung bei Auswertung von mindestens drei konsekutiven Markern: ca. 12,8 kb bzw. 91,6 kb (minimale Regionen))
– oben: Oligonukleotid-Array-CGH-Marker: reduzierte Intensität
– Mitte: SNP-Marker: relative Allelwerte / B-allele-frequencies mit loss of heterozygosity, zwei statt drei Allelwolken in deletierter Region
– unten: Ideogramm Chromosom 12 mit betroffener Region
d Array-CGH: partielle Trisomie 4q34.3-qter
– oben: Oligonukleotid-Array-CGH-Marker: erhöhte Intensität
– Mitte: SNP-Marker: relative Allelwerte / B-Allele frequencies mit vier statt drei Allelwolken in duplizierter Region
– unten: Ideogramm Chromosom 4 mit betroffener Region